同位素標(biāo)記與未標(biāo)記化合物的含量如何測(cè)定?
同位素標(biāo)記化合物的合成和生產(chǎn)中,很難獲得純品,如氘代、14C、15N等標(biāo)記的化合物通常含有一定量的未標(biāo)記化合物,雖然質(zhì)譜法是檢測(cè)和定量標(biāo)記化合物的最廣泛和最直接的方法,但是標(biāo)記和未標(biāo)記的化合物的各種同位素的A和A+1,…,A+n峰的質(zhì)譜峰信號(hào)重疊相互重疊,使得尤其是存在多個(gè)標(biāo)記位置的環(huán)或存在Cl、Br元素的化合物,他們的質(zhì)譜信號(hào)重疊更為復(fù)雜,即使是使用高分辨率的質(zhì)譜系統(tǒng)(如TOF、Orbitrap)也難以準(zhǔn)確解決定量的問題。
盡管一些文獻(xiàn)報(bào)道中提出了各種質(zhì)譜信號(hào)的重疊校正方案,但即使在50%(50﹕50)高濃度的標(biāo)記與未標(biāo)記混合物,其校正誤差也大于±10%,這使得對(duì)5-10%的低濃度的混合物的可靠定量幾乎不可能實(shí)現(xiàn)的。
通過MassWorks的TrueCalTM技術(shù)對(duì)測(cè)量的質(zhì)譜信號(hào)峰進(jìn)行峰形校正,來提高質(zhì)譜系統(tǒng)對(duì)同位素峰型的譜圖準(zhǔn)確度(Spectral Accuracy),以確保使用多元最小二乘法擬合能從校準(zhǔn)的質(zhì)譜圖中計(jì)算出每個(gè)同位素峰的“真實(shí)”貢獻(xiàn)。
考察兩種同位素峰分布復(fù)雜度不同的化合物:第一種是含有一個(gè)Cl原子的D2標(biāo)記化合物——Hydrochlorothiazide-3,3-d2 (HCT-d2),第二種是含有兩個(gè)Cl原子且14C 標(biāo)記在苯環(huán)上的化合物——雙氯酚酸鈉。選擇了三種質(zhì)譜系統(tǒng)來評(píng)儀器定量分析同位素標(biāo)記物的的適用性:ThermoFisher LTQ/Orbitrap、Agilent LC/MSD和WatersXevo TQ LC/MSMS。 在每個(gè)MS系統(tǒng)上,首先在Profile模式下測(cè)量純的未標(biāo)記化合物,然后將其進(jìn)行峰形校正,以評(píng)估可實(shí)現(xiàn)的譜圖準(zhǔn)確度。 再利用譜圖準(zhǔn)確度,對(duì)同位素標(biāo)記的兩種化合物進(jìn)行計(jì)算來獲得它們中含有的各種標(biāo)記和未標(biāo)記離子的相對(duì)濃度。
D2標(biāo)記含Cl化合物——HCT-d2
未標(biāo)記的HCT(C7H6N3O4S2Cl)在LTQ/Orbitrap下采集的Profile模式數(shù)據(jù),使用MassWorks處理,獲得的譜圖準(zhǔn)確度約為97.3%(見圖1),標(biāo)記后的HCT-d2的譜圖準(zhǔn)確度又有明顯下降,僅為96.2%,將D2標(biāo)記和未標(biāo)記的HCT按50%:50%混合后的譜圖準(zhǔn)確度下降更為嚴(yán)重,只能達(dá)到92.5%(見圖2),導(dǎo)致的結(jié)果就是MassWorks給出的兩者的相對(duì)濃度出現(xiàn)了±10%的誤差,這種誤差下要準(zhǔn)確計(jì)算標(biāo)記和未標(biāo)記的含量顯然是不可能的。
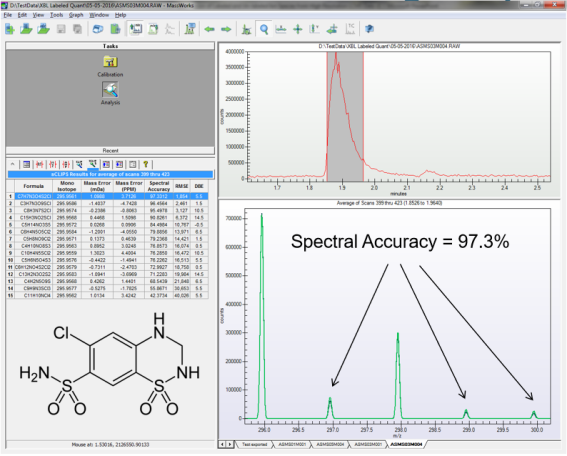
圖1 MassWorks軟件在LTQ/Orbitrap下測(cè)定的HCT(C7H6N3O4S2Cl)的同位素譜圖準(zhǔn)確度
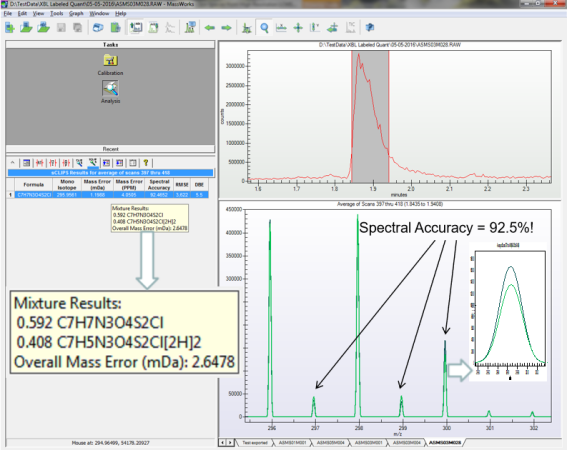
圖2 MassWorks軟件在LTQ/Orbitrap下測(cè)定的HCT-d2(C7H4N3O4S2ClD2)的同位素譜圖準(zhǔn)確度
將測(cè)試轉(zhuǎn)移到單四極桿的Agilent LC/MSD系統(tǒng)上,測(cè)得的未標(biāo)記的HCT的譜圖準(zhǔn)確度高達(dá)99.0%,標(biāo)記的HCT-d2的譜圖準(zhǔn)確度為98.9%,50%:50%混合物的譜圖準(zhǔn)確度為98.7%(見圖3),結(jié)果表明,單四極桿的LC/MSD的同位素譜圖準(zhǔn)確度測(cè)定準(zhǔn)確。然后進(jìn)一步考察HCT和HCT-d2按不同比例混合的MassWokrs定量測(cè)試效果,每一個(gè)濃度測(cè)定3次,然后數(shù)據(jù)對(duì)比實(shí)際的混合濃度和MassWorks軟件計(jì)算出來濃度值,結(jié)果見圖4,結(jié)果表明,平均濃度誤差反映了測(cè)量偏差或系統(tǒng)偏差均小于0.6%,且要小于標(biāo)準(zhǔn)偏差(SD<1%)。HCT-d2的實(shí)際混合濃度值與軟件計(jì)算值的線性相關(guān)系數(shù)R2=0.9996,預(yù)測(cè)的標(biāo)準(zhǔn)誤差SEP=0.53%。
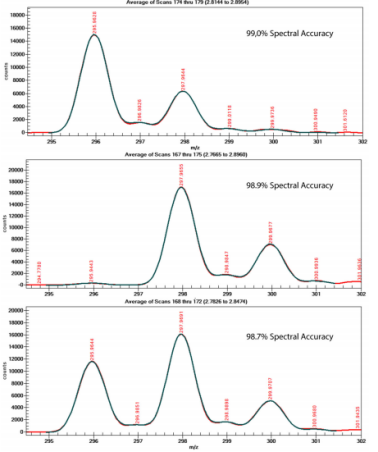
圖3 未標(biāo)記的HCT(上)、標(biāo)記的HCT-d2(中)、HCT/HCT-d2= 50:50的混合物(下),紅色曲線為校正的同位素譜圖,黑色為理論的同位素譜圖
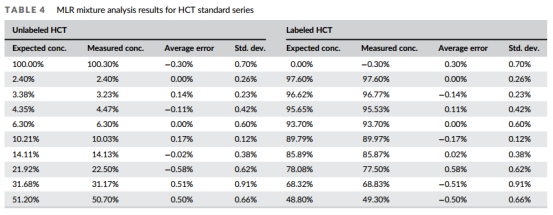
圖4 使用MassWorks的分析得到的不同濃度HCT的定量分析結(jié)果
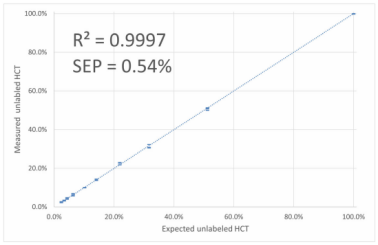
圖5 HCT-d2的計(jì)算濃度與實(shí)際濃度的線性關(guān)系
14C標(biāo)記含Cl化合物——HCT-d2
雙氯芬酸鈉(C14H10NO2Cl2Na),含有2個(gè)Cl原子,苯環(huán)上可被標(biāo)記的14C的數(shù)量為0~6個(gè),14C標(biāo)記后的化合物的同位素峰分布比HCT-d2更為復(fù)雜,使用LTQ/Orbitrap應(yīng)對(duì)7種潛在共存混合物的準(zhǔn)確定量任務(wù)來說是一個(gè)挑戰(zhàn)。然而,當(dāng)用Waters Xevo TQ LC/MSMS測(cè)量時(shí),從供應(yīng)商購買的放射性的14C標(biāo)記化合物的譜圖準(zhǔn)確度達(dá)到了98.9%(見圖6),MassWorks軟件計(jì)算出來的0~6個(gè)14C標(biāo)記化合物的各自的濃度比(圖7),計(jì)算出來的總的放射性比活性為62.6%,這與供應(yīng)商提供的62.7 mCi/mmol值非常一致。圖8為按不同比例混合的標(biāo)記和未標(biāo)記化合物的定量分析結(jié)果,標(biāo)記物的混合濃度值與軟件計(jì)算濃度值的線性相關(guān)系數(shù)R2=0.9989,預(yù)測(cè)的標(biāo)準(zhǔn)誤差SEP=1.98%。
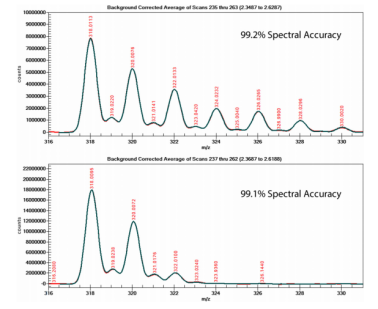
圖6 未標(biāo)記雙氯酚酸鈉(上)和標(biāo)記的雙氯酚酸鈉(下)的譜圖準(zhǔn)確度結(jié)果
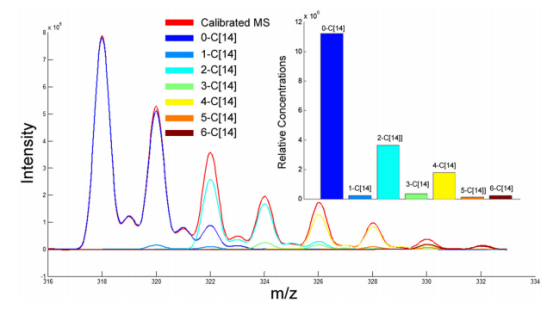
圖7 MassWorks給出的標(biāo)記的雙氯酚酸鈉的校正質(zhì)譜圖及其中所有化合物的相對(duì)含量
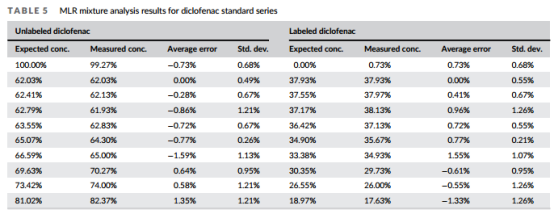
圖8 使用MassWorks的多元線性分析得到的不同濃度雙氯芬酸鈉的定量分析結(jié)果
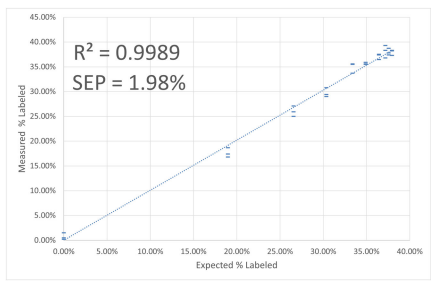
圖9 雙氯芬酸鈉14C標(biāo)記物的計(jì)算濃度與實(shí)際濃度的線性關(guān)系
關(guān)于MassWorks 軟件
MassWorks軟件是由 Cerno Bioscience 公司開發(fā)的一款革命性的MS數(shù)據(jù)定性分析軟件,能幫助我們?cè)诘头直媛实乃臉O桿GC/MS、LC/MS直接測(cè)定化合物的精確質(zhì)量,并通過獨(dú)有的譜圖準(zhǔn)確度概念確定出準(zhǔn)確的分子式。MassWorks軟件同樣適用于高分率質(zhì)譜(TOF、Orbitrap)的定性分析。
關(guān)于綠綿科技
綠綿科技是Cerno Bioscience公司在中國區(qū)的總代理商,負(fù)責(zé)Cerno公司旗下的MassWorks、GC/ID 等產(chǎn)品市場(chǎng)推廣、銷售、售前/售后技術(shù)支持、應(yīng)用支持。
若您想了解獲取 MassWorks 產(chǎn)品的更多信息或應(yīng)用,歡迎致電綠綿科技!
關(guān)于綠綿科技
北京綠綿科技有限公司(簡稱:綠綿科技)以體現(xiàn)客戶服務(wù)價(jià)值為宗旨,以專業(yè)精神和技能為廣大實(shí)驗(yàn)室分析工作者提供樣品前處理、樣品制備及分析、實(shí)驗(yàn)數(shù)據(jù)精確分析和管理的全面解決方案,致力于協(xié)助客戶提高分析檢測(cè)的效率和水平。主要代理產(chǎn)品聯(lián)系電話:010-82676061/2/3/4/5/6/7/8
E-mail:[email protected]。
